- DANEELpath es un sistema de análisis de imagen basado en inteligencia artificial para estudiar modelos 3D de neuroblastoma
- La herramienta, de acceso libre, ya se está utilizando también en otros tumores pediátricos, nuevos fármacos y estrategias terapéuticas

De izquierda a derecha: Rosa Noguera, Isaac Vieco, Sofía Granados y Samuel Navarro.
Investigadores del Instituto de Investigación Sanitaria INCLIVA y de la Universitat de València (UV) han desarrollado DANEELpath, una herramienta de código abierto (open source) de análisis de imagen que permite estudiar de forma automatizada modelos tridimensionales (3D) de neuroblastoma, un cáncer infantil del sistema nervioso simpático que aparece principalmente durante los primeros cinco años de vida.
La herramienta se integra como extensión en el software de patología digital QuPath y combina inteligencia artificial con técnicas de morfología matemática para analizar imágenes histológicas. Al ser de acceso abierto, cualquier investigador puede consultar su funcionamiento, modificar el código y compartirlo con otros equipos científicos.
DANEELpath permite automatizar la caracterización de modelos 3D de neuroblastoma y obtener datos de forma más rápida y reproducible, lo que facilita su uso en investigación y en evaluación preclínica de posibles tratamientos.
Comprender mejor el comportamiento del tumor
El tumor es una estructura compleja y su agresividad no depende solo de las células malignas, sino también del microambiente que las rodea. En este contexto, la matriz extracelular -la red de proteínas que rodea a las células- y algunos de sus componentes pueden convertirse en dianas terapéuticas.
En trabajos previos del grupo, la vitronectina, una proteína presente en la matriz extracelular, ha destacado por su papel en la adhesión celular y su asociación con comportamientos tumorales más agresivos, lo que la sitúa como una posible diana terapéutica. Para estudiar este proceso de forma controlada, el laboratorio ha desarrollado modelos 3D biomiméticos que reproducen el entorno del tumor permiten reproducir entornos con o sin vitronectina y testar fármacos dirigidos a bloquear sus interacciones celulares.
Sin embargo, el principal cuello de botella era el análisis de las secciones histológicas generadas por estos modelos. Este proceso podría requerir hasta tres días de trabajo para analizar una sola imagen, lo que limitaba la cantidad de datos que podían obtenerse.
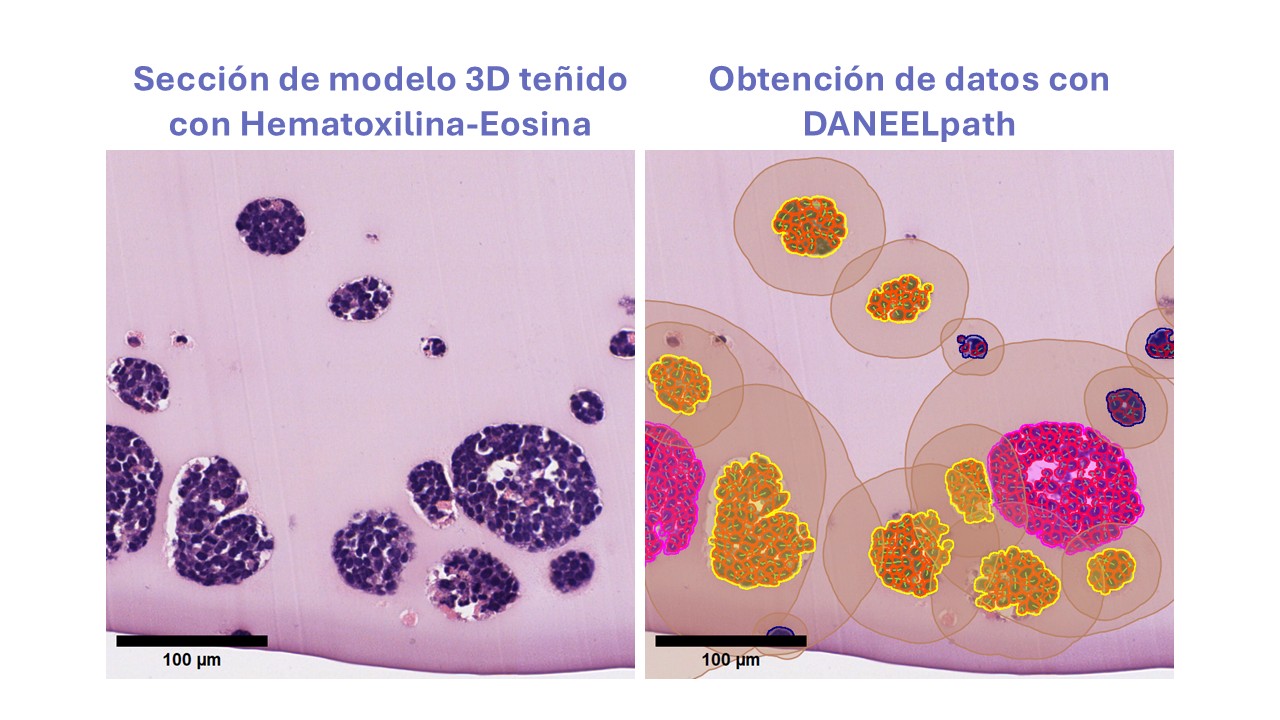
De días de trabajo a minutos
La investigación, publicada en la revista Scientific Reports con el título ‘DANEELpath open source digital analysis tools for histopathological research in neuroblastoma models’, presenta el desarrollo y la validación de esta herramienta. DANEELpath permite extraer datos cuantitativos a partir de las secciones histológicas de modelos 3D de forma rápida y ajustada. Gracias al uso de redes neuronales, el proceso de segmentación de conglomerados celulares pasa de requerir días de trabajo a completarse en cuestión de minutos.
Además, la herramienta permite cuantificar la expresión de vitronectina y analizar la distribución espacial de las células en imágenes completas del tejido, lo que facilita un estudio más detallado del comportamiento tumoral.
Estos datos ya se están empleando para evaluar el impacto de la vitronectina en múltiples líneas celulares de neuroblastoma, incluidas líneas comerciales y otras derivadas de pacientes, dentro de modelos tridimensionales. Además, DANEELpath se está usando para evaluar los cambios morfológicos y de organización celular provocados por fármacos dirigidos a bloquear las interacciones entre las células tumorales y la vitronectina.
Los investigadores destacan que la utilidad de DANEELpath no se limita al neuroblastoma de alto riesgo. La herramienta se está utilizando en otros modelos 3D de tumores pediátricos, como el sarcoma de Ewing, y podría aplicarse en el futuro a la evaluación de otros fármacos y estrategias terapéuticas.
Equipo investigador y financiación
El trabajo ha sido realizado por el Grupo de Investigación Traslacional en Tumores Sólidos Pediátricos de INCLIVA. Entre los autores se encuentran Isaac Vieco Martí, investigador predoctoral con beca FPU; Sofía Granados Aparici y Amparo López-Carrasco, investigadoras postdoctorales; y el doctor Samuel Navarro, catedrático de Patología de la Universitat de València.
La investigación ha sido dirigida por la doctora Rosa Noguera, catedrática de Histología de la Universitat de València, coordinadora del citado grupo de INCLIVA e investigadora principal de uno de los grupos de CIBERONC (Centro de Investigación Biomédica en Red de Cáncer), del Instituto de Salud Carlos III.
Este estudio ha sido financiado por el Instituto de Salud Carlos III de Madrid/FEDER (PI20/01107), CIBERONC (CB16/12/00484), Fundación Neuroblastoma (PRV/00166) y el Ministerio de Ciencia Innovación y Universidades de España (beca FPU20/05344).
Referencia del artículo: https://www.nature.com/articles/s41598-026-37134-5
Demostración DANEELpath: https://www.youtube.com/watch?v=rr7qY1bVEHw
Repositorio GitHub: https://github.com/iviecomarti/qupath-extension-daneelpath